
- by 浩瑞研发
基因组重测序
基因组重测序对已有参考基因组物种的不同个体进行基因组测序,并以此为基础进行个体或群体水平的遗传差异分析。通过全基因组重测序,研究者可以找到大量的单核苷酸多态性位点(SNP)、拷贝数变异(CNV)、插入缺失(InDel)、结构变异( SV)等变异位点 ,应用到各个领域。
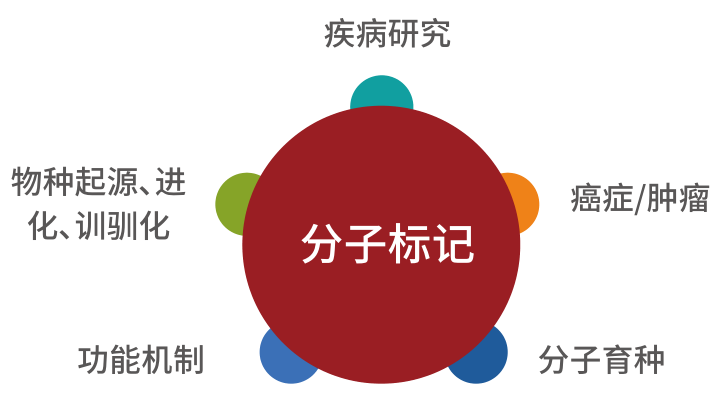
动植物重测序(农学)
在个体层面,基因组水平的结构变异能够影响基因的功能, 以致影响个体表型性状。
在群体层面上,SVs可能为生物体及其后代提供适应优势,最终使这些变异有机会在正选择压力下适应甚至固定在群体中,从而改变其进化轨迹。
结构变异在物种进化中也起着重要作用,基于SNP的重测序研究瓶颈,研究方向逐渐转向基于大尺度SV的关联分析,高分文章频发。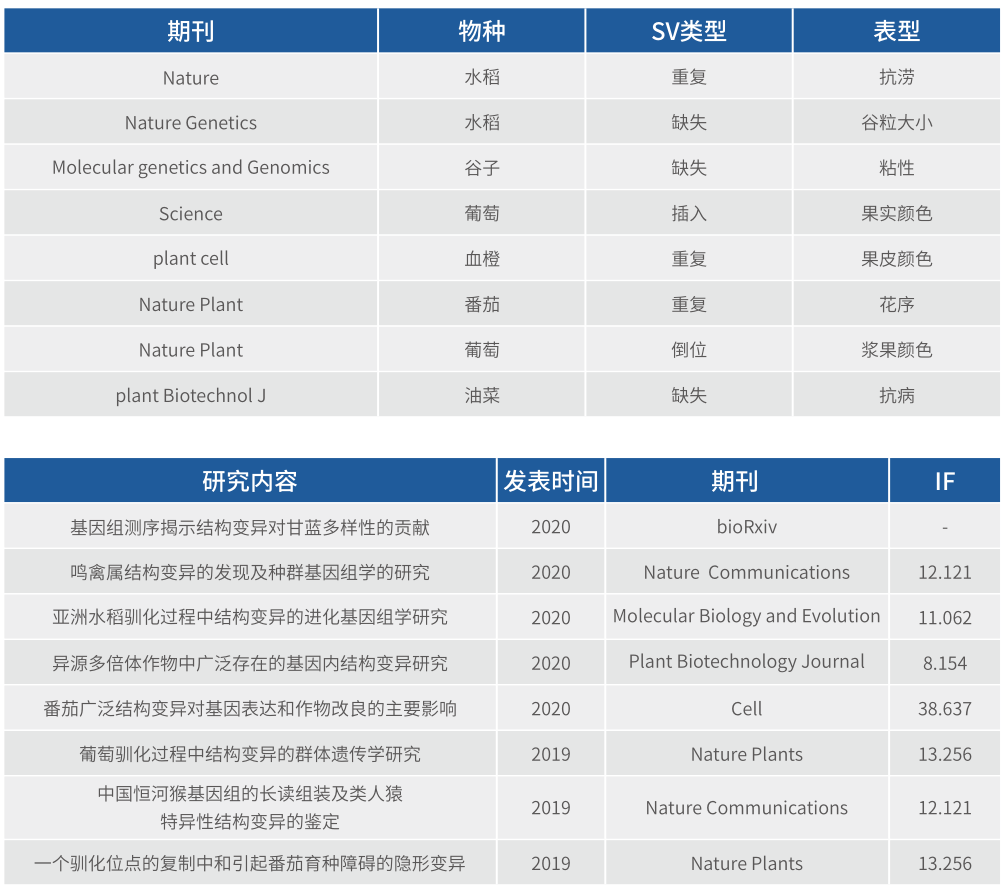
技术路线
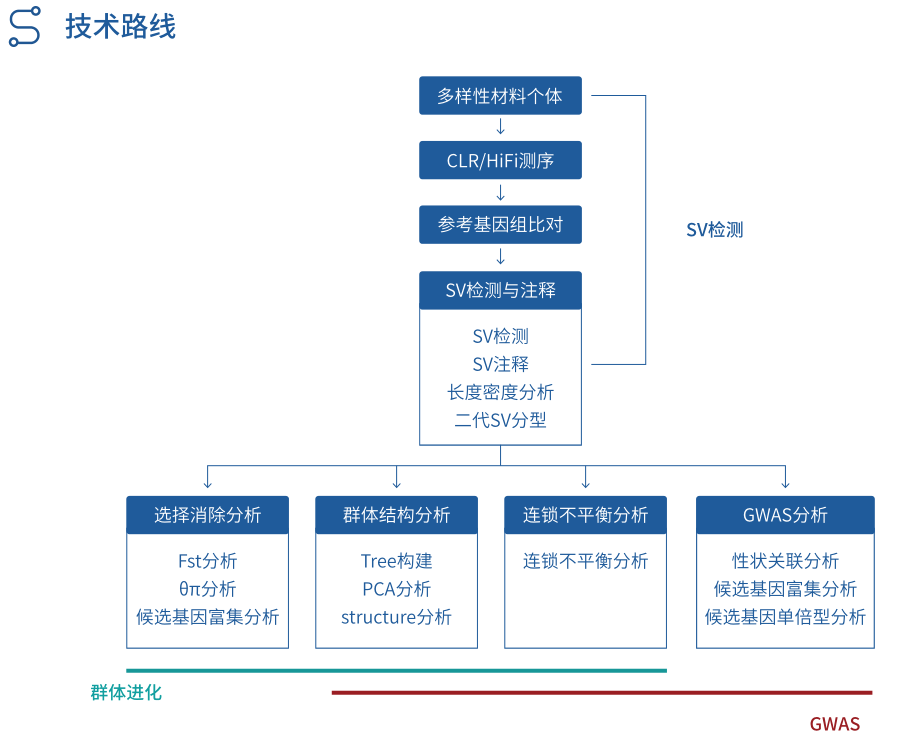
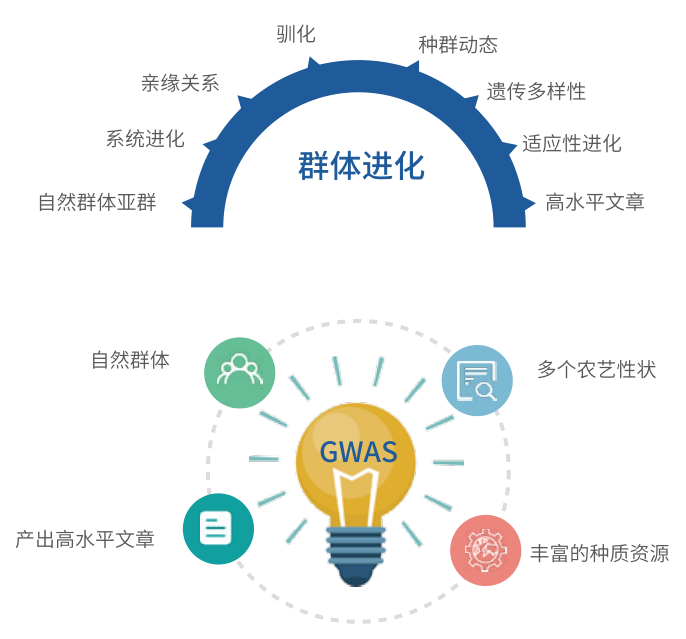
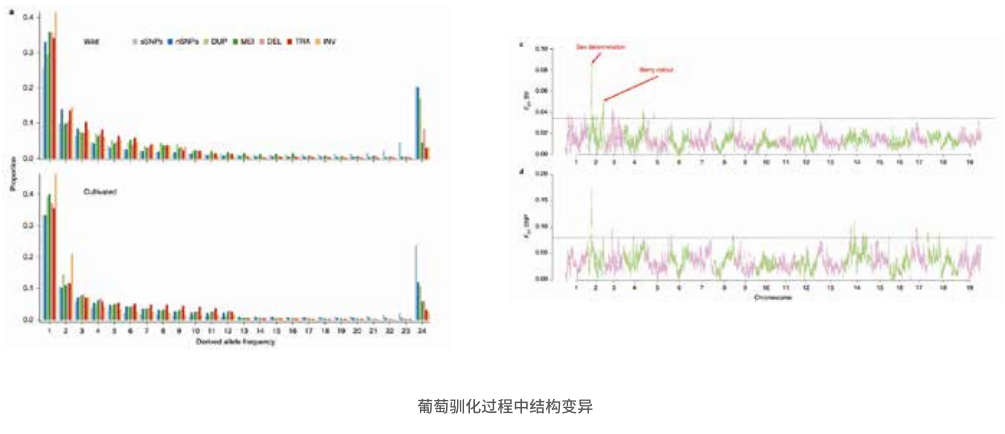
案例1:三代测序揭示葡萄驯化过程中结构变异的群体遗传学

研究背景:结构变异体(SVs)是植物基因组中一个很大程度上未被探索的特征,本研究通过调查野生和驯化葡萄中SV的群体遗传来填补我们对植物基因组进化认知的空白。
研究方法:利用三代测序+二代测序+Hi-C技术,组装了高杂合葡萄霞多丽品种的基因组序(Char04),用长、短reads比对和全基因组比对等方法,综合比较Char04和Cab08两基因组之间的SVs;以Char04为参考基因组,以Char04和Cab08综合比对的交叉SVs集合为金标准,收集有代表性的 50 个栽培葡萄品种和 19 个野生亲缘品种的短读长测序数据,进行群体间 SVs 的高度筛选。
研究结果:以同义SNP作为中性选择的标志,对比栽培种和野生种之间的SVs频率,所有的SVs类型都表现出位点频谱分析(SFS)相对于同义SNP的左移,结果表明,SVs都经历了强烈的纯化选择,INV和TRA事件尤其有害。另外,研究发现性别决定及浆果颜色相关的SVs。
人的基因组重测序(医学)
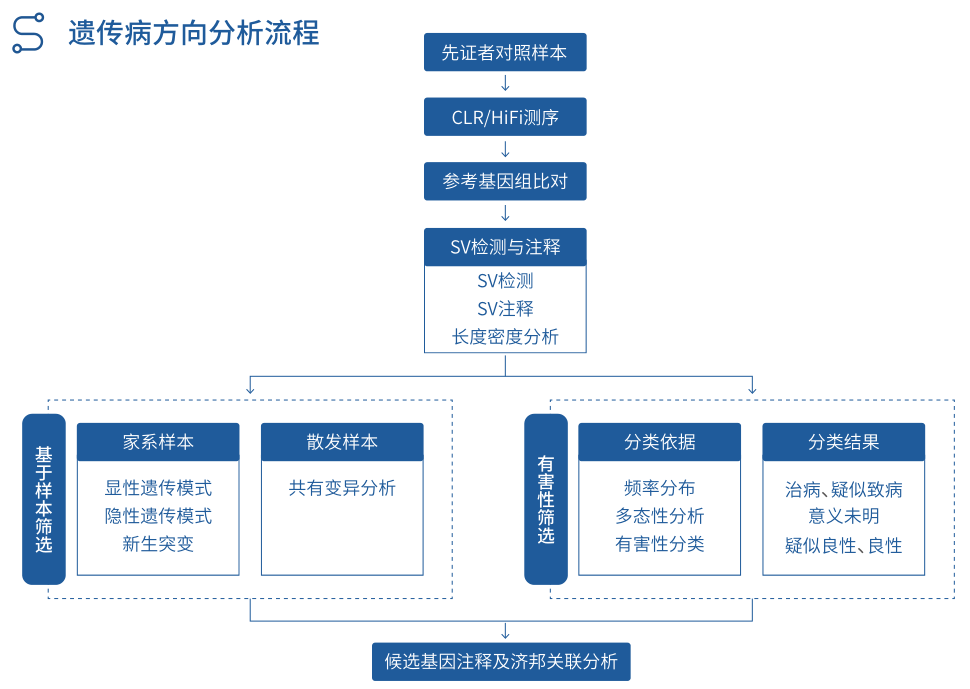
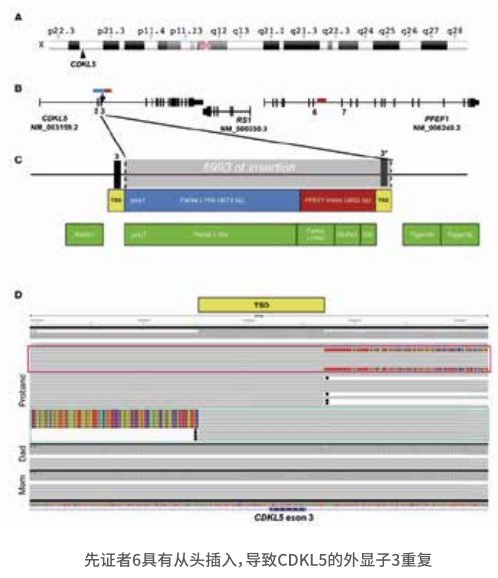
遗传病 SV 中“万里挑一”
1.在最初实验设计或者样本筛选上,尽可能地考虑周全,除对 先 证 者 进行三代人重测序外,尽可能同时包含其 父母 和 同 胞兄妹 ,这样比较容易全面的找到致病变异。
2.过滤方式多样化:遗传模式筛选、数据库过滤。
3.验证回溯,临床表型匹配,遗传模式匹配,其他测序手段辅助验证或实验验证。
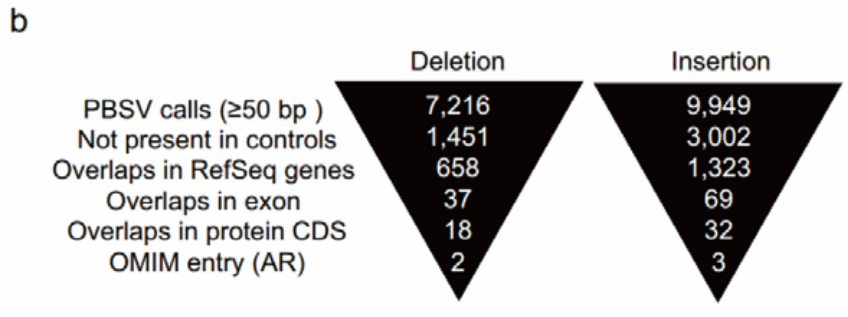
案例2:揭示揭示人类基因组遗传多样性

研究背景:瞄准当前人类基因组注释中的缺陷,深度挖掘人类基因组SVs,并对SVs进行分类解析,揭示人类基因组遗传多样性 。
研究方法:使用PacBio长读长测序技术对11个人类基因组进行测序,添加2个之前已研究过的葡萄胎(胎盘绒毛发生良性病变的胚胎CHM1和CHM13)及2个亚洲人基因组数据,平均测序深度>50×;
研究结果:非洲样本多态性最丰富,平均每一个非洲人样本贡献了11.1%的特异性SVs,而非非洲人样本平均是5.6%;绝大多数SV代表真正的人类多态性,但其中507个共有和主要SV仅检测到替代等位基因,表明该位点为极端次要等位基因或错误。

- by 浩瑞研发
基因组重测序
基因组重测序对已有参考基因组物种的不同个体进行基因组测序,并以此为基础进行个体或群体水平的遗传差异分析。通过全基因组重测序,研究者可以找到大量的单核苷酸多态性位点(SNP)、拷贝数变异(CNV)、插入缺失(InDel)、结构变异( SV)等变异位点 ,应用到各个领域。

动植物重测序(农学)
在个体层面,基因组水平的结构变异能够影响基因的功能, 以致影响个体表型性状。
在群体层面上,SVs可能为生物体及其后代提供适应优势,最终使这些变异有机会在正选择压力下适应甚至固定在群体中,从而改变其进化轨迹。
结构变异在物种进化中也起着重要作用,基于SNP的重测序研究瓶颈,研究方向逐渐转向基于大尺度SV的关联分析,高分文章频发。
技术路线


案例1:三代测序揭示葡萄驯化过程中结构变异的群体遗传学

研究背景:结构变异体(SVs)是植物基因组中一个很大程度上未被探索的特征,本研究通过调查野生和驯化葡萄中SV的群体遗传来填补我们对植物基因组进化认知的空白。
研究方法:利用三代测序+二代测序+Hi-C技术,组装了高杂合葡萄霞多丽品种的基因组序(Char04),用长、短reads比对和全基因组比对等方法,综合比较Char04和Cab08两基因组之间的SVs;以Char04为参考基因组,以Char04和Cab08综合比对的交叉SVs集合为金标准,收集有代表性的 50 个栽培葡萄品种和 19 个野生亲缘品种的短读长测序数据,进行群体间 SVs 的高度筛选。
研究结果:以同义SNP作为中性选择的标志,对比栽培种和野生种之间的SVs频率,所有的SVs类型都表现出位点频谱分析(SFS)相对于同义SNP的左移,结果表明,SVs都经历了强烈的纯化选择,INV和TRA事件尤其有害。另外,研究发现性别决定及浆果颜色相关的SVs。

人的基因组重测序(医学)

遗传病 SV 中“万里挑一”
1.在最初实验设计或者样本筛选上,尽可能地考虑周全,除对 先 证 者 进行三代人重测序外,尽可能同时包含其 父母 和 同 胞兄妹 ,这样比较容易全面的找到致病变异。
2.过滤方式多样化:遗传模式筛选、数据库过滤。
3.验证回溯,临床表型匹配,遗传模式匹配,其他测序手段辅助验证或实验验证。

案例2:揭示揭示人类基因组遗传多样性

研究背景:瞄准当前人类基因组注释中的缺陷,深度挖掘人类基因组SVs,并对SVs进行分类解析,揭示人类基因组遗传多样性 。
研究方法:使用PacBio长读长测序技术对11个人类基因组进行测序,添加2个之前已研究过的葡萄胎(胎盘绒毛发生良性病变的胚胎CHM1和CHM13)及2个亚洲人基因组数据,平均测序深度>50×;
研究结果:非洲样本多态性最丰富,平均每一个非洲人样本贡献了11.1%的特异性SVs,而非非洲人样本平均是5.6%;绝大多数SV代表真正的人类多态性,但其中507个共有和主要SV仅检测到替代等位基因,表明该位点为极端次要等位基因或错误。


- by 浩瑞研发
基因组重测序
基因组重测序对已有参考基因组物种的不同个体进行基因组测序,并以此为基础进行个体或群体水平的遗传差异分析。通过全基因组重测序,研究者可以找到大量的单核苷酸多态性位点(SNP)、拷贝数变异(CNV)、插入缺失(InDel)、结构变异( SV)等变异位点 ,应用到各个领域。

动植物重测序(农学)
在个体层面,基因组水平的结构变异能够影响基因的功能, 以致影响个体表型性状。
在群体层面上,SVs可能为生物体及其后代提供适应优势,最终使这些变异有机会在正选择压力下适应甚至固定在群体中,从而改变其进化轨迹。
结构变异在物种进化中也起着重要作用,基于SNP的重测序研究瓶颈,研究方向逐渐转向基于大尺度SV的关联分析,高分文章频发。
技术路线


案例1:三代测序揭示葡萄驯化过程中结构变异的群体遗传学

研究背景:结构变异体(SVs)是植物基因组中一个很大程度上未被探索的特征,本研究通过调查野生和驯化葡萄中SV的群体遗传来填补我们对植物基因组进化认知的空白。
研究方法:利用三代测序+二代测序+Hi-C技术,组装了高杂合葡萄霞多丽品种的基因组序(Char04),用长、短reads比对和全基因组比对等方法,综合比较Char04和Cab08两基因组之间的SVs;以Char04为参考基因组,以Char04和Cab08综合比对的交叉SVs集合为金标准,收集有代表性的 50 个栽培葡萄品种和 19 个野生亲缘品种的短读长测序数据,进行群体间 SVs 的高度筛选。
研究结果:以同义SNP作为中性选择的标志,对比栽培种和野生种之间的SVs频率,所有的SVs类型都表现出位点频谱分析(SFS)相对于同义SNP的左移,结果表明,SVs都经历了强烈的纯化选择,INV和TRA事件尤其有害。另外,研究发现性别决定及浆果颜色相关的SVs。

人的基因组重测序(医学)

遗传病 SV 中“万里挑一”
1.在最初实验设计或者样本筛选上,尽可能地考虑周全,除对 先 证 者 进行三代人重测序外,尽可能同时包含其 父母 和 同 胞兄妹 ,这样比较容易全面的找到致病变异。
2.过滤方式多样化:遗传模式筛选、数据库过滤。
3.验证回溯,临床表型匹配,遗传模式匹配,其他测序手段辅助验证或实验验证。

案例2:揭示揭示人类基因组遗传多样性

研究背景:瞄准当前人类基因组注释中的缺陷,深度挖掘人类基因组SVs,并对SVs进行分类解析,揭示人类基因组遗传多样性 。
研究方法:使用PacBio长读长测序技术对11个人类基因组进行测序,添加2个之前已研究过的葡萄胎(胎盘绒毛发生良性病变的胚胎CHM1和CHM13)及2个亚洲人基因组数据,平均测序深度>50×;
研究结果:非洲样本多态性最丰富,平均每一个非洲人样本贡献了11.1%的特异性SVs,而非非洲人样本平均是5.6%;绝大多数SV代表真正的人类多态性,但其中507个共有和主要SV仅检测到替代等位基因,表明该位点为极端次要等位基因或错误。


